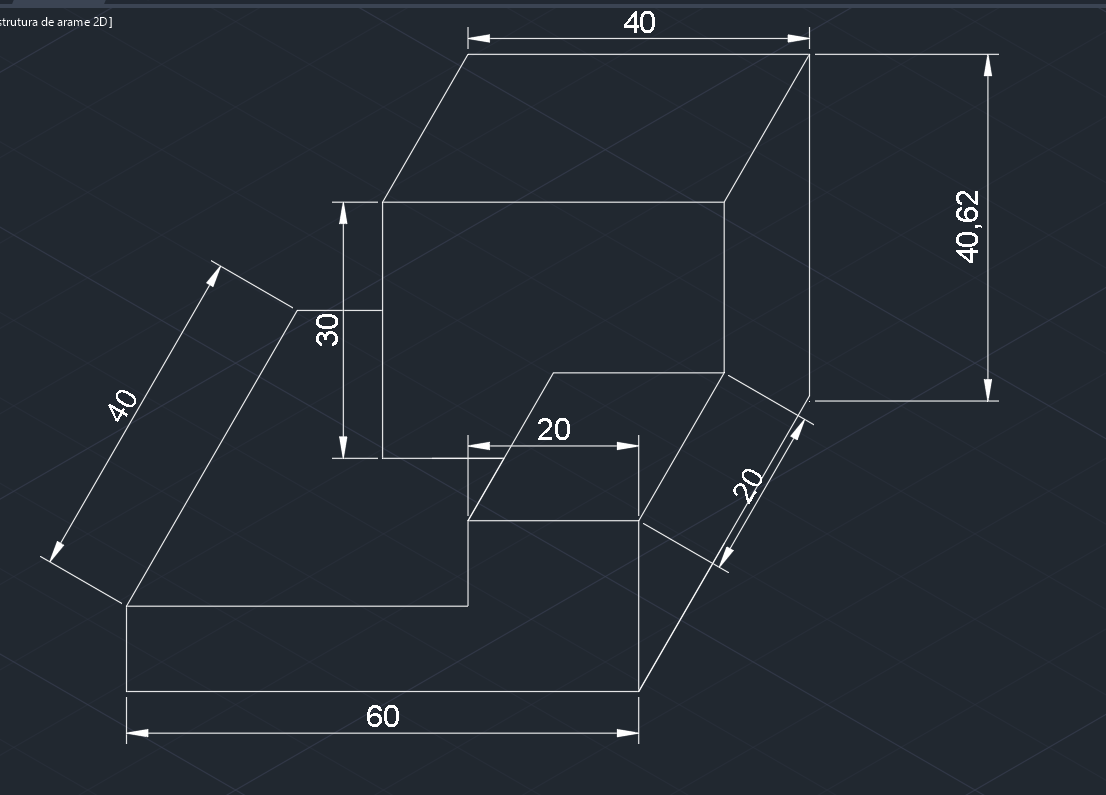
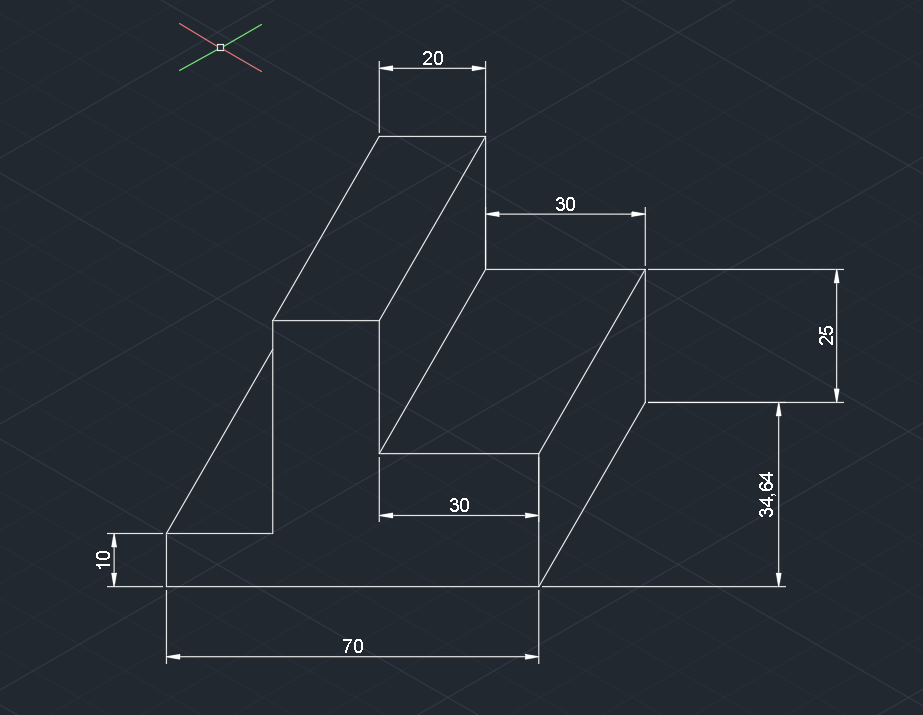
Projeto Hemacias
No dia de hoje 15/10/2023 , foram criadas novas amostras (30 ) de treinamento de 3 hemácias diferentes.
Totalizando agora 60 amostras de treino.
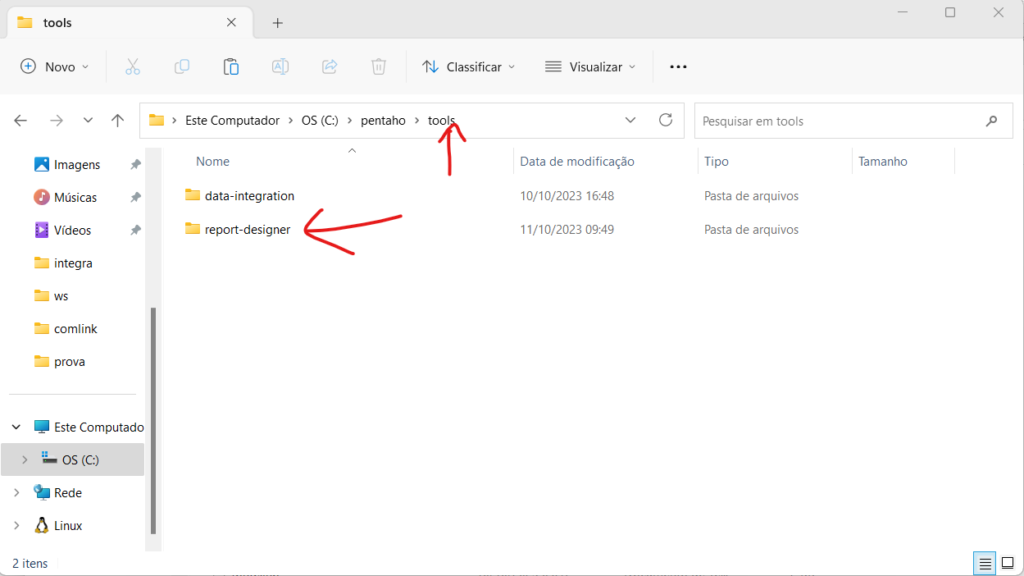
Adicionei um projeto em python para gerar as imagens cinza a partir das imagens coloridas.
Para isso basta rodar o código em hemacias\python\tools\converte\converte.py
Conforme o código abaixo em python.
# -*- coding: utf-8 -*-
"""
Spyder Editor
This is a temporary script file.
"""
import os
from PIL import Image
def converter_imagens_cinza(diretorio_entrada, diretorio_saida):
# Verifica se o diretório de saída existe. Se não, cria-o.
if not os.path.exists(diretorio_saida):
os.makedirs(diretorio_saida)
# Percorre os arquivos no diretório de entrada
for filename in os.listdir(diretorio_entrada):
print(f"filename:{filename}")
# Verifica se o arquivo é uma imagem .jpg
if filename.lower().endswith(".jpg"):
# Cria os caminhos completos de entrada e saída para o arquivo
caminho_entrada = os.path.join(diretorio_entrada, filename)
caminho_saida = os.path.join(diretorio_saida, filename)
# Abre a imagem
with Image.open(caminho_entrada) as img:
# Converte a imagem para cinza
img_cinza = img.convert("L")
# Salva a imagem convertida no diretório de saída
img_cinza.save(caminho_saida)
print(f"Imagem {filename} convertida para cinza e salva em {caminho_saida}.")
# Converte imagens em positivas coloridas testes:
diretorio_entrada = "D:/projetos/maurinsoft/hemacias/fotos/positivas coloridas testes"
diretorio_saida = "D:/projetos/maurinsoft/hemacias/fotos/positivas cinza testes"
converter_imagens_cinza(diretorio_entrada, diretorio_saida)
# Converte imagens em positivas coloridas treino:
diretorio_entrada = "D:/projetos/maurinsoft/hemacias/fotos/positivas coloridas treino"
diretorio_saida = "D:/projetos/maurinsoft/hemacias/fotos/positivas cinza treino"
converter_imagens_cinza(diretorio_entrada, diretorio_saida)
print('Finalizou\n')O programa gera as saídas responsáveis pelas imagens de treino.
O Fonte deste projeto, pode ser visto no github: